ブログ
英語論文ゼミ: 最新のタンパク質-リガンド複合体構造予測法「Boltz-2」

2026年4月2日の第1回英語論文ゼミでは、以下の論文を紹介しました。
“Boltz-2: Towards Accurate and Efficient Binding Affinity Prediction”
「Boltz-2: 正確かつ効率的な結合親和性予測を目指して」
掲載先
本論文は、生物学分野のプレプリントリポジトリであるbioRxiv(バイオアーカイブ)で公開された論文です(※プレプリント:学術誌による査読(Peer review)プロセスを経て公開される前の暫定版・速報版の研究論文 )。bioRxivは、生理学、生化学、薬理学、微生物学、遺伝学、バイオインフォマティクスなど、生物学に関する幅広い分野の研究成果を掲載しています。
論文の概要
本論文は、タンパク質-リガンドの複合体立体構造を高精度かつ高速に予測し、さらにその結合親和性も予測できる深層学習ツール Boltz-2 を新たに開発したことを報告しています。
化学物質がどのタンパク質に、どのように結合するかは、創薬や毒性学において非常に重要な情報です。そのため、タンパク質-リガンド複合体の立体構造や結合親和性を高精度に予測する技術は、近年ますます注目されています。タンパク質立体構造予測の分野は、2024年にノーベル化学賞の対象ともなったAlphaFold2の登場をきっかけに急速に発展しており、今回紹介するBoltz-2もその流れの中で注目を集めている最新手法の一つです。
Boltz-2が従来法と比べて特に注目される点は、①立体構造予測精度、②結合親和性予測精度、③計算速度の3つです。著者らのベンチマークでは、Boltz-2はタンパク質-リガンド複合体の構造予測において高い性能を示し、AlphaFold3と比較しても競争力のある結果が報告されています。また、立体構造の物理的妥当性の面でも良好な成績が示されています。
さらに、結合親和性予測についても高い性能が報告されており、従来高精度とされる自由エネルギー摂動法(FEP)と比べて、大幅に短い計算時間で予測できる点が大きな特徴です。FEPでは計算に数時間から数日を要することもありますが、Boltz-2ではより短時間で予測を行える可能性があります。
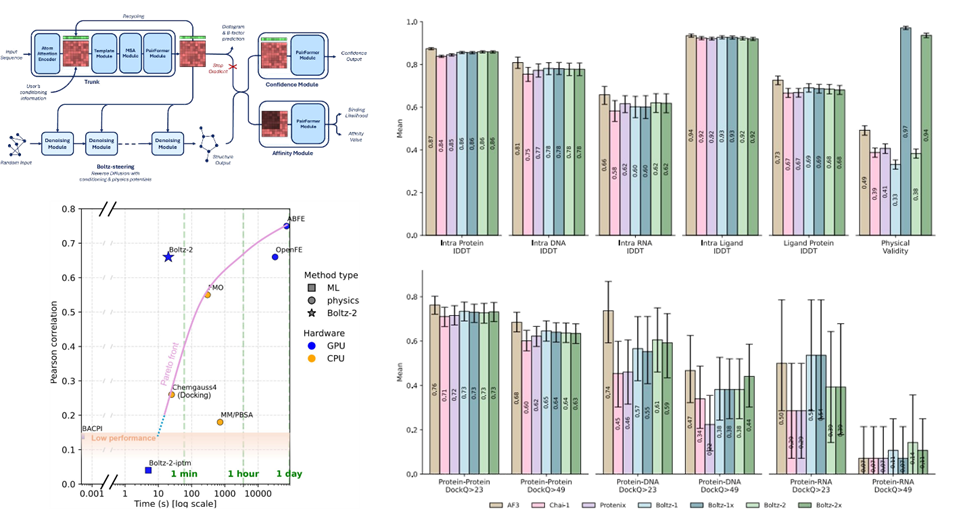
図.Boltz-2のアーキテクチャおよびベンチマーク。Passaro S, Corso G, Wohlwend J, et al. “Boltz-2: Towards Accurate and Efficient Binding Affinity Prediction” bioRxiv, 2025, doi:10.1101/2025.06.14.659707 の Figures 1–3 をマージ・再構成。CC BY 4.0 ライセンスの下で利用。
Saro Passaro, Gabriele Corso, Regina Barzilay, et al. Boltz-2: Towards Accurate and Efficient Binding Affinity Prediction
bioRxiv 2025.06.14.659707; doi: https://doi.org/10.1101/2025.06.14.659707 Licensed under CC BY 4.0
ラボメンバーからの質問例
Q. Boltz-2の臨床応用までの課題についてどう考えられますか?
A. Boltz-2に限らず、シミュレーション手法は一般に臨床段階そのものというより、その前段階にあたるスクリーニングで活用されることが多いです。創薬や毒性評価では、まず多数の候補物質の中から有望なものを絞り込む必要があります。その段階で、複合体構造や結合親和性を高精度かつ高速に予測できれば、実験の効率化やコスト削減につながり、その後の開発成功率の向上にも寄与すると考えられます。
この論文を選んだ理由
私の研究テーマは、今回のBoltz-2のような深層学習ツールや分子ドッキングなどの構造生物学的シミュレーションを駆使して、化学物質の未知の毒性を解き明かす手法を開発することです。化学物質の毒性機序を理解するうえで、標的タンパク質との複合体立体構造および結合親和性は重要なファクターです。
Boltz-2は、構造生物学の知見を深層学習モデルに巧みに取り入れることで、構造および親和性を高精度かつ高速に予測しようとする点に大きな特徴があります。この最新手法の原理について理解を深めることは、自身の研究の発展にも大いに寄与すると考え、この論文を選びました。
また、Boltz-2は私以外の後輩ラボメンバーも利用し始めている手法であり、ゼミを通じてその原理を共有することで、ラボ全体の研究レベルの底上げにもつながると考えています。
出典論文
Saro Passaro, Gabriele Corso, Regina Barzilay, et al.
Boltz-2: Towards Accurate and Efficient Binding Affinity Prediction
bioRxiv 2025.06.14.659707
https://doi.org/10.1101/2025.06.14.659707
Jumper, J., Evans, R., Pritzel, A. et al.
Highly accurate protein structure prediction with AlphaFold
Nature 596, 583–589 (2021).
https://doi.org/10.1038/s41586-021-03819-2
Abramson, J., Adler, J., Dunger, J. et al.
Accurate structure prediction of biomolecular interactions with AlphaFold 3
Nature 630, 493–500 (2024).
https://doi.org/10.1038/s41586-024-07487-w
最新ブログ
アーカイブ
- 2026年4月 (3)
- 2025年7月 (6)
- 2025年6月 (2)
- 2025年5月 (2)
- 2025年4月 (4)
- 2025年3月 (4)
- 2025年2月 (1)
- 2025年1月 (2)
- 2024年12月 (1)
- 2024年11月 (3)
- 2024年10月 (5)
- 2024年9月 (1)
- 2024年8月 (1)
- 2024年7月 (4)
- 2024年6月 (1)
- 2024年4月 (1)
- 2024年2月 (1)
- 2024年1月 (1)
- 2023年11月 (1)
- 2023年10月 (1)
- 2023年6月 (1)
- 2023年4月 (1)
- 2023年3月 (1)
- 2022年12月 (1)
- 2022年11月 (1)
- 2022年9月 (1)
- 2022年6月 (1)
- 2022年3月 (3)
- 2022年1月 (1)
- 2021年12月 (3)
- 2021年11月 (1)
- 2021年10月 (1)
- 2021年9月 (1)
- 2021年8月 (1)
- 2021年7月 (3)